
文章正文简要报道

近日,华中师范大学物理科学与技术学院赵蕴杰教授与美国达特茅斯计算机学院Soroush Vosoughi教授、美国乔治华盛顿大学曾辰教授合作在软凝聚态与生物物理领域取得了新的研究进展,在《Nature Communications》发表题为“Evaluating native-like structures of RNA-protein complexes through the deep learning method”的研究论文。华中师范大学博士研究生曾成伟为该论文的第一作者,达特茅斯计算机学院简弋人为共同第一作者,物理科学与技术学院赵蕴杰教授为论文的通讯作者,华中师范大学为第一完成单位。

DRPScore模型训练中学习的RNA-蛋白质复合物特征与4DCNN深度学习模型
赵蕴杰教授课题组发展了基于人工智能和统计物理模型相结合的新方法DRPScore。该方法通过分子对接模拟复合物结合的构象变化,可以考虑柔性对接中分子结构的变化。另一方面,该方法聚焦于RNA-蛋白质相互作用界面,通过4DCNN模型不仅可以有效学习原子质量、原子电荷、相互作用类型(静电相互作用、氢键等)和相互作用距离的局部特征,还可以学习复合物二级结构相互作用(RNA为配对、发卡环和内环等;蛋白质为螺旋和beta折叠单元)与口袋拓扑结构等全局特征。
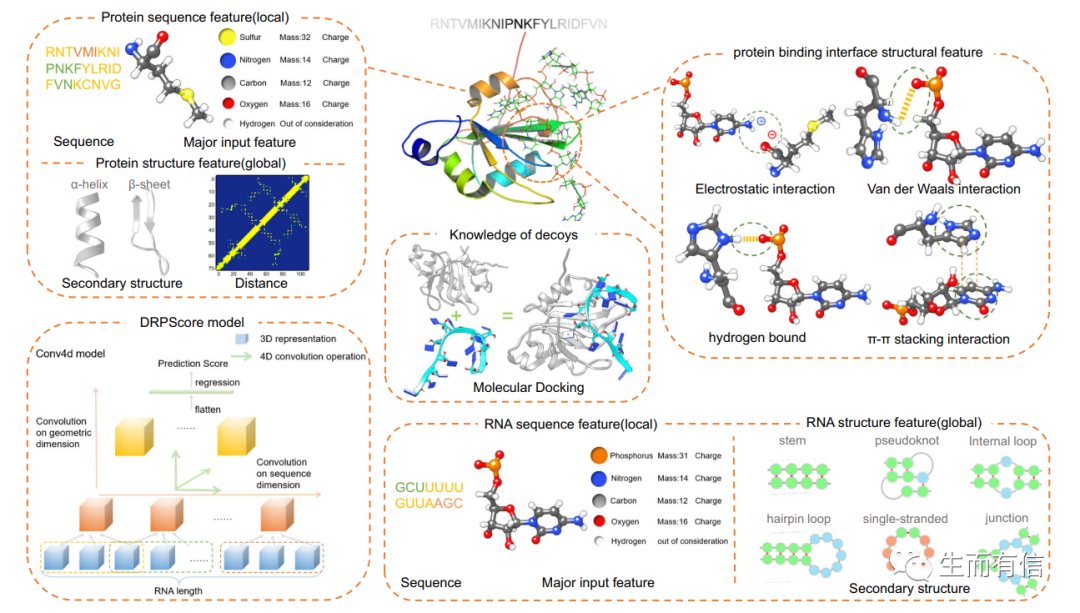
DRPScore模型训练中学习的RNA-蛋白质复合物特征与4DCNN深度学习模型
柔性对接测试集结果
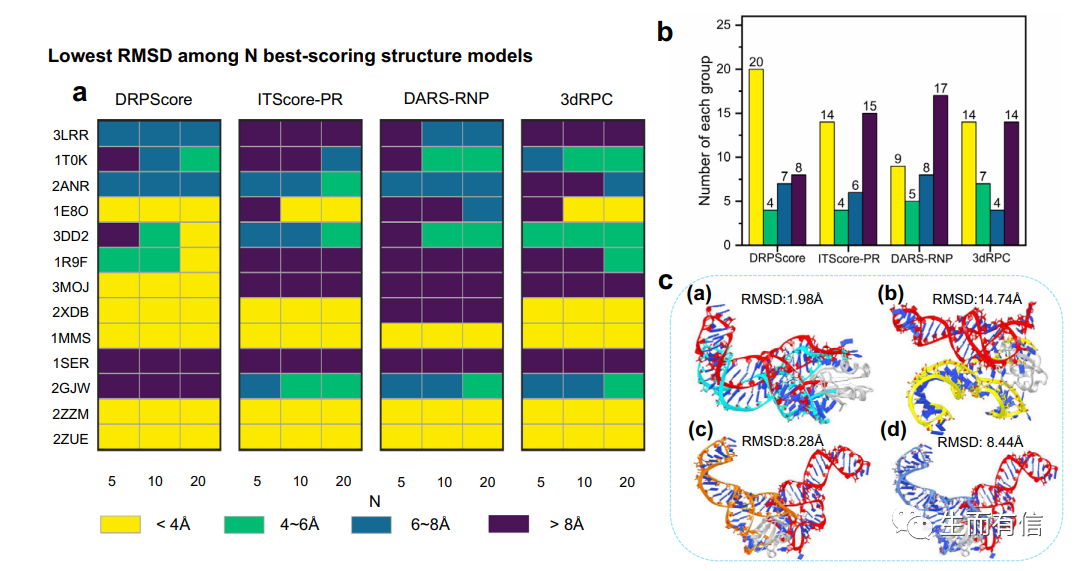
柔性对接测试集结果(黄色为近天然态结构,DRPScore的预测精度显著高于传统模型)
结语
– 通讯作者简介 –
华中师范大学
赵蕴杰
教授
——— End ———
关于湖北省生物信息学会:
湖北省生物信息学会,是由湖北省内从事生物信息学科技工作者自愿组成的全省性、学术性、非营利性的社会团体。学会致力于制定生物信息学专业规范,加强学术交流与合作,推动人才培养,促进理事单位及省内外生物信息学产业的健康可持续发展。

